Science | 浙大林世贤团队开发一种稀有密码子重编码技术,实现非天然氨基酸高效、高保真度编码
进入 #重新认识分子互作仪阅读更多话题内容
导读:该研究工作提出使用特定的稀有密码子代替空白密码子用于遗传编码非天然氨基酸的新思路,设计并开发了名为“稀有密码子重编码”的非天然氨基酸编码体系。
不同于20种天然氨基酸,非天然氨基酸具有多样化的侧链基团,可以赋予蛋白质更优的或全新的物理、化学或生物特性。经过过去二十多年的研究积累,人们利用遗传密码子拓展技术(Genetic Code Expansion,GCE)已经成功实现了300多种非天然氨基酸的遗传编码。然而,由于释放因子与识别终止密码子的tRNA的强烈竞争,这种方法在哺乳动物细胞中效率低下,限制了其广泛应用。

2024年6月7日,浙江大学林世贤研究员课题组在Science发表了题为“Rare codon recoding for efficient noncanonical amino acid incorporation in mammalian cells”的研究论文,提出使用特定的稀有密码子代替空白密码子用于遗传编码非天然氨基酸的新思路,设计并开发了名为“稀有密码子重编码”(Rare Codon Recoding, RCR)的非天然氨基酸编码体系。
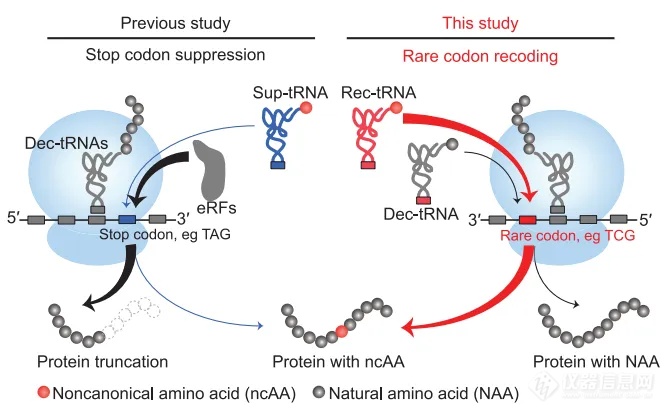
哺乳动物细胞中ncAA结合的罕见密码子编码示意图(Credit: Science)
通过系统的工程改造和核酸序列的大数据模型预测,稀有密码子重编码技术以接近天然氨基酸的编码效率高效合成系列带有非天然氨基酸的功能蛋白质,并在哺乳动物细胞中首次成功合成带有6个位点非天然氨基酸和4种不同类型非天然氨基酸的蛋白质,充分展示了稀有密码子重编码体系的优越性。
浙江大学生命科学研究院博士后丁文龙、博士生于微和博士后陈宇霖是论文的共同第一作者,林世贤研究员是论文的通讯作者。
2024年10月17日下午,于微博士将在“顶刊相见| MST分子互作技术前沿进展”主题研讨会进行成果分享,欢迎报名预约席位:https://www.instrument.com.cn/webinar/meetings/nanotemper241017/

来源于:仪器信息网
热门评论
最新资讯
新闻专题