推荐厂家
暂无
暂无

 400-860-5168转3737
400-860-5168转3737
 留言咨询
留言咨询

 400-877-2799
400-877-2799
 留言咨询
留言咨询

 400-628-5299
400-628-5299
 留言咨询
留言咨询



[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析中建模样品优选方法的研究 作者:王丽杰,郭建英,徐可欣 摘要:结合牛奶成分[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]测量系统的实例,在已定的浓度范围内针对牛奶中脂肪、蛋白质、乳糖三成分采用正交设计法优选参与建模的样品。研究中首次利用正交表的“正交性”原理优选建模样品,并针对牛奶中脂肪浓度的测量采用偏最小二乘(PLS)回归方法交互验证方式建立模型。在此基础上,将正交设计样品集与常规方法选择的样品集的脂肪PLS模型的预测结果进行了对比。实验结果表明:采用正交设计样品集与常规样品集分别建立的PLS模型的预测偏差之差低于0.02g/100g,上述两种方法PLS模型的实际预测浓度与参考浓度之差均集中在0.1g/100g,而后者样品数量约为前者的七倍。进一步的实验结果表明:从常规样品集的样品中随机抽取与正交设计样品集的样品数量相同的样品作为随机样品集并建模,其PLS模型的预测偏差高于常规方法的两倍、相关系数相对较低,并且其实际预测浓度与参考浓度之差集中在0.4g/100g。关键词:近红(NIR)光谱分析;正交设计法;正交性;牛奶;偏最小二乘(PI )回归引言 [url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]的数据处理分析通常由三部分构成:建模样品(校正集样品)的选择及光谱的预处理、定性或定量模型的建立、未知样品组成或性质的预测。由于校正集样品的选择及其基础数据测量的准确性直接关系到所建模型的适用性和测试结果的准确性,因此,校正集样品的选择是[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]数据处理及分析的关键环节。 校正集样品的选择过程中,样品的光谱特征及其性质范围应能涵盖以后未知样品的光谱特征。为保证校正模型的稳健性,校正集的样品数一般不应低于50个,且在所测的浓度或性质范围内,样品的个数应该是均匀分布的【l】。通常校正集样品的确定有常规选择和计算机识别两种方法【l】。常规选择是根据样品光谱的积累和性质或组成数据的分布来选择建立校正集的样品,并通过部分样品进行验证。计算机识别则是纯粹通过确定的计算模型,用计算机来识别所采集样品的光谱间差距,确定适合校正集的样品。依照常规方法建立校正样品集,其最大缺点是必须积累大量的样品以供选择。而计算机识别方法在很大程度上减少了常规方法测量基础数据的样品数,降低了建模费用,但仍然存在一定的缺陷:1)仍然要收集大量的样品谱图以便于判断选择;2)有些光谱的差异并非完全由所测样品的组成或性质差异引起,可能是某些随机因素如样品的温度、粒径大小、物粒形态等因素的差异造成;3)对不同的性质在最佳样品集的选择上可能存在差异,而仅从光谱的差异上有时难以体现;4)对那些含量较低的成分,其量的变化对整个谱图而言往往并不明显,此时如光谱处理方法不合理,也难以选出合适的样品集。 针对上述情况,研究中首次提出了一种利用正交表的“正交性”原理优选校正集样品的方法,并结合牛奶的[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]测量的实例对其可行性进行了探讨,该方法的研究对于光谱分析中校正集样品的优化选择具有重要的研究价值。1 校正样品集选择方法 正交设计法是以相关专业知识及概率论和数理统计为基础,利用数学上的“正交性”原理编制并已标准化的表格——正交表来科学安排试验方案、并对试验结果进行计算、分析、找出最优或较优的条件的数学方法。 利用正交表安排试验方案搭配均衡具有代表性,因为对全体因素而言,正交设计是一种部分试验,但对于其中任何两个因素而言确是带有等重复的全面试验。由于正交试验设计要求任何两个因素是全面试验,因此试验点在优选区的分布是均匀分布的,每个试验点都有强烈的代表性,能够比较全面地反映优选区内的大致情况,并能保证主要因素的各种可能搭配都不会漏掉。 研究中采用正交表的“正交性”原理选择校正集样品。结合牛奶成分[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]测量系统的开发(系统测量原理图见图1所示),采用L8l 9 3正交表进行校正集样品优选。根据牛奶中脂肪、蛋白质及乳糖等成分浓度的常规范围确定相应浓度(单位:g/100g)范围分别为:脂肪:2.5~5.5,蛋白质:2.8~4.8,乳糖:4.4~5.4。在上述浓度范围内,根据典型样品浓度特性设计脂肪、蛋白质及乳糖3因素、9水平(脂肪:2.5、2.87、3.24、3.61、3.98、4.35、4.72、5.09、5.46,蛋白质:2.8、3.05、3.3、3.55、3.8、4.05、4.3、4.55、4.8,乳糖:4.4、4.52、4.64、4.76、4.88、5、5.12、5.24、5.36)浓度分配方案,共计81个样品。不考虑成分因素间的交互作用,采用上述方案选择校正样品集样品的脂肪、蛋白质及乳糖三成分浓度空间散点图见图2,其中脂肪与蛋白质两成分散点图见图3。(图略)2 实验与数据分析 采用自制系统样机,针对不同区域、不同种类、不同季节及不同哺乳时期奶牛的牛奶漫反射光谱进行收集整理,共得407个样品光谱。将其作为备用样品集,从中选取与正交设计方案中的样品浓度最接近的样品共计61个(以脂肪为准)作为正交设计校正样品集。然后,针对正交设计校正样品集和全校正样品集(将407个样品全部作为校正集样品)采用偏最d'-乘(PLS)方法交互验证方式分别建立脂肪的校正模型,并应用这两种模型分别对全部407个样品的脂肪浓度进行实际预测,交互验证及实际预测参数见表1,407个样品中脂肪浓度的实际预测值与参考值间的对比结果见表2。 从表l可以看出:正交设计校正样品集与全校正样品集的交互验证结果中,交互验证相关系数 相差0.0038、交互验证均方根偏差(Root Mean Square Error ofCross Validation,RMSECV)相差0.0195,预测相关系数 相差o.0032、预测均方根偏差(Rot Mean Square Error ofPrediction,RMSEP)相差0.0173。采用PLS校正模型分别对全部407个样品进行实际预测时,相关系数 相差0.0015、RMSEP相差0.0112。从表2可以看出:正交设计校正样品集与全校正样品集对所有407个样品的实际预测浓度与参考浓度间的偏差均集中在O.1g/100g左右。表l、表2同时列出了全部样品中随机选取的61个样品作为校正集(称为随机校正样品集)的PLS1模型的交互验证结果及其对全部407个样品的实际预测结果,从中可以看出随机校正样品集的预测偏差是全校正样品集的预测偏差的两倍、相关系数相对降低,并且随机校正样品集对所有407个样品的实际预测浓度与参考浓度间的偏差集中在0.4左右。3 小结 实验结果表明:正交设计校正样品集与全校正样品集的预测偏差之差在0.02g/100g以内,实际预测浓度与参考浓度间的偏差均集中在O.1g/100g左右,而正交设计校正样品集中样品数量是全校正样品集的样品数量的七分之一。进一步的实验结果表明:随机校正样品集的预测偏差是全校正样品集预测偏差的两倍、且相关系数相对降低,其实际预测浓度与参考浓度间的偏差集中在0.4g/100g左右。 可见,正交设计校正集样品(61个)在全部样品中具有代表性,如果将81个样品光谱全部收集作为正交设计校正样品集,预计预测偏差将会进一步缩小。因此,利用正交表的“正交性”原理进行建模过程中校正集样品的优选具有实用性,该方法的研究不仅为[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析中校正集样品的优选提供了可参考的方法,而且对于校正模型的优化及提高测试结果的准确性等方面均具有重要的意义。
[img]http://www.instrument.com.cn/bbs/images/affix.gif[/img][url=http://www.instrument.com.cn/bbs/download.asp?ID=70146]人参总皂贰[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]及定标建模分析[/url]
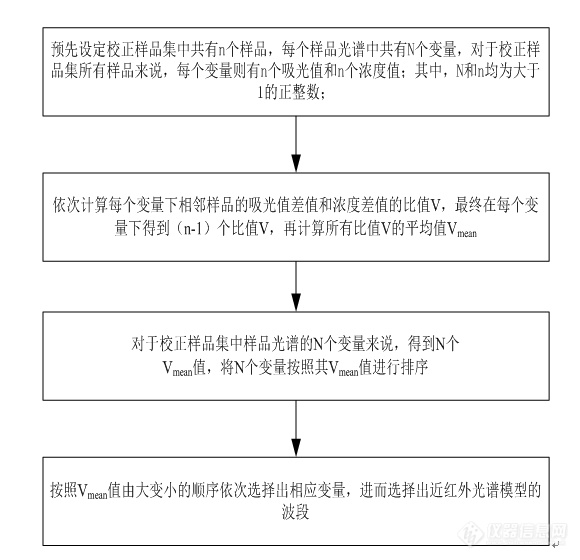
[align=center][b]基于“吸光度-浓度变化率”波段选择方法提高[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模能力[/b][/align][url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]定量分析是一种二级分析方法,利用校正模型对未知含量或性质参考值的样品基于[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]数据进行预测,以测定未知待测样品的浓度或性质参考值,根据预测结果评价模型的预测能力和有效性。由于[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]吸收峰严重重叠,信号吸收较弱,背景干扰严重。因此需要运用波段选择方法提取有效波段,常用的波段选择方法包括前向间隔偏最小二乘法(forwardintervalpartialleastsquares, FiPLS)、反向间隔偏最小二乘法(backwardintervalpartialleastsquares, BiPLS),相关系数法(correlationcoefficient, CC)和无信息变量消除算法(uninformativevariableelimination, UVE)等。本实验对近红外建模物质的浓度与吸光度的变化率进行研究,提出了新的波段选择方法:“吸光度-浓度变化率”方法(Ratioof absorbance to concentration,RATC),弥补了常用波段选择的缺陷,构建了血浆蛋白含量检测模型。1材料1.1试剂血浆样品(山东泰邦生物制品有限公司,中国);去离子水。1.2仪器和软件AntarisⅡ傅里叶变换[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱仪[/color][/url],液体采样附件;液体玻璃小管(4×50mm,KimbleChase 德国);Matlab2015a(美国Mathworks公司);PLS_Toolbox工具箱(美国EigenvectorResearch)。2方法2.1光谱采集采用傅里叶变换[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱仪[/color][/url](Antaris II FT-NIR)液体温控透射采样模块,控制温度为37℃下,采集原料人血浆样品光谱。光谱扫描范围和分辨率为10000-4000cm[sup]-1[/sup]和8cm[sup]-1[/sup],扫描次数为32次,参比为空气,每隔1小时校正背景。实验室环境为温度26℃,湿度30%。2.2 校正集验证集划分方法需要划分校正集和验证集的样品:原料人血浆样品20份,[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模属性为总蛋白含量值;2.3 数据处理及模型建立研究采用MATLAB2015a数学软件以及PLS_Toolbox 1.95工具箱对光谱数据进行处理,对建模物质的吸光度和浓度进行变化率分析,选出用于建模的波数点,针对[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析技术的建模分析,以验证均方根误差(RMSEP)值作为其建模预测能力的主要指标。通过讨论不同物质的[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析模型建模结果,验证所提波段选择方法的可行性和应用性。3 “吸光度-浓度变化率”波段选择原理及方法本文提出了一种[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型的波段选择方法,基于“吸光度浓度变化率”对校正样品集中所有样品进行波段选择,其具体过程为:步骤1:预先设定校正样品集中共有n个样品,每个样品光谱中共有N个变量,对于校正样品集所有样品来说,每个变量则有n个吸光值和n个浓度值;其中,N和n均为大于1的正整数;步骤2:依次计算每个变量下相邻样品的吸光值差值和浓度差值的比值V,最终在每个变量下得到(n-1)个比值V,再计算所有比值V的平均值V[sub]mean[/sub];V[sub]i[/sub]=|(A[sub]i[/sub]-A[sub]i[/sub][sub]+[/sub][sub]1[/sub])|/(C[sub]i[/sub]-C[sub]i[/sub][sub]+[/sub][sub]1[/sub]) (1)V[sub]mean[/sub]=[img=,50,50]https://bbs.instrument.com.cn/xheditor/xheditor_skin/blank.gif[/img] (2)A[sub]i[/sub]表示第i个样品的吸光值,A[sub]i[/sub][sub]+[/sub][sub]1[/sub]表示第i+1样品的吸光值;C[sub]i[/sub]表示第i个样品的浓度值,C[sub]i[/sub][sub]+[/sub][sub]1[/sub]表示第i+1个样品的浓度值;V[sub]1[/sub]表示第1个样品与其相邻的第2个样品的吸光值差值和浓度差值的比值;V[sub]2[/sub]表示第2个样品与其相邻的第3个样品的吸光值差值和浓度差值的比值;V[sub]3[/sub]表示第3个样品与其相邻的第4个样品的吸光值差值和浓度差值的比值;V[sub]4[/sub]表示第4个样品与其相邻的第5个样品的吸光值差值和浓度差值的比值;V[sub]n[/sub][sub]-[/sub][sub]1[/sub]表示第n-1个样品与其相邻的第n个样品的吸光值差值和浓度差值的比值。步骤3:对于校正样品集中样品光谱的N个变量来说,得到N个V[sub]mean[/sub]值,将N个变量按照其V[sub]mean[/sub]值进行排序;步骤4:按照V[sub]mean[/sub]值由大变小的顺序依次选择出相应变量,直至所有变量全部选完,停止建模,记录所有情况的建模结果。其中,V[sub]mean[/sub]值越大,则代表吸光值因浓度变化所产生的响应越大,同时V[sub]mean[/sub]即为所提出的波段选择方法的关键值,命名为“吸光度-浓度变化率”值。从V[sub]mean[/sub]值最大的变量开始建模,随后按照V[sub]mean[/sub]值由大变小的顺序,采取依次增加一个变量的方法,开始建立[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型,简化流程图如图4-1所示。[align=center][img=,580,560]https://ng1.17img.cn/bbsfiles/images/2019/08/201908161623164821_3386_3237657_3.png!w580x560.jpg[/img][/align][align=center]图4-1“吸光度-浓度变化率”波段选择方法简化流程图[/align]具体应用例证如图4-2所示:校正样品集有20个样品,其浓度值分别为C[sub]1[/sub],C[sub]2[/sub],…,C[sub]20[/sub]。[align=center][img=,670,461]https://ng1.17img.cn/bbsfiles/images/2019/08/201908161623371131_5892_3237657_3.png!w670x461.jpg[/img][/align][align=center]图4-2“吸光度-浓度变化率”波段选择方法具体例证过程[/align]本文将所提出的波段选择方法用于血浆蛋白含量检测模型的构建中,讨论血浆蛋白含量变化同样品吸光度之间的变化率,进而选择合适的波段用于建模。[b]4 实验结果4.1 近红外建模样品集划分[/b]对三种样品进行校正集和验证集的划分结果如表4-1所示,其结果全部满足验证集的参数值范围在校正集之内,同时对于不同样品的不同属性的校正集和验证集来说,其平均值和标准偏差值也比较接近,满足[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模校正集和验证集的划分要求。[align=center]表4-1不同样品不同属性的校正集验证集数据统计结果[/align] [table][tr][td] [align=center]样品[/align] [align=center](检测参数) [/align] [/td][td] [align=center]样品集[/align] [/td][td] [align=center]样本数[/align] [/td][td] [align=center]最大值[/align] [/td][td] [align=center]最小值[/align] [/td][td] [align=center]平均值[/align] [/td][td] [align=center]标准偏差[/align] [/td][/tr][tr][td=1,2] [align=center]原料人血浆[/align] [align=center](蛋白含量值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]15[/align] [/td][td] [align=center]76.80[/align] [/td][td] [align=center]40.56[/align] [/td][td] [align=center]59.34[/align] [/td][td] [align=center]12.31[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]5[/align] [/td][td] [align=center]73.16[/align] [/td][td] [align=center]41.89[/align] [/td][td] [align=center]57.56[/align] [/td][td] [align=center]11.65[/align] [/td][/tr][tr][td=1,2] [align=center]玉米[/align] [align=center](水分值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]60[/align] [/td][td] [align=center]10.99[/align] [/td][td] [align=center]9.38[/align] [/td][td] [align=center]10.22[/align] [/td][td] [align=center]0.39[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]20[/align] [/td][td] [align=center]10.94[/align] [/td][td] [align=center]9.64[/align] [/td][td] [align=center]10.27[/align] [/td][td] [align=center]0.36[/align] [/td][/tr][tr][td=1,2] [align=center]玉米[/align] [align=center](蛋白质含量值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]60[/align] [/td][td] [align=center]3.83[/align] [/td][td] [align=center]3.09[/align] [/td][td] [align=center]3.50[/align] [/td][td] [align=center]0.18[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]20[/align] [/td][td] [align=center]3.82[/align] [/td][td] [align=center]3.18[/align] [/td][td] [align=center]3.48[/align] [/td][td] [align=center]0.18[/align] [/td][/tr][tr][td=1,2] [align=center]玉米[/align] [align=center](油脂值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]60[/align] [/td][td] [align=center]9.71[/align] [/td][td] [align=center]7.66[/align] [/td][td] [align=center]8.73[/align] [/td][td] [align=center]0.53[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]20[/align] [/td][td] [align=center]9.60[/align] [/td][td] [align=center]8.11[/align] [/td][td] [align=center]8.49[/align] [/td][td] [align=center]0.32[/align] [/td][/tr][tr][td=1,2] [align=center]玉米[/align] [align=center](淀粉值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]60[/align] [/td][td] [align=center]66.47[/align] [/td][td] [align=center]62.83[/align] [/td][td] [align=center]64.62[/align] [/td][td] [align=center]0.90[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]20[/align] [/td][td] [align=center]65.60[/align] [/td][td] [align=center]63.63[/align] [/td][td] [align=center]64.91[/align] [/td][td] [align=center]0.48[/align] [/td][/tr][tr][td=1,2] [align=center]汽油[/align] [align=center](辛烷值)[/align] [/td][td] [align=center]校正集[/align] [/td][td] [align=center]45[/align] [/td][td] [align=center]89.60[/align] [/td][td] [align=center]83.40[/align] [/td][td] [align=center]87.15[/align] [/td][td] [align=center]1.57[/align] [/td][/tr][tr][td] [align=center]验证集[/align] [/td][td] [align=center]15[/align] [/td][td] [align=center]88.70[/align] [/td][td] [align=center]84.50[/align] [/td][td] [align=center]87.25[/align] [/td][td] [align=center]1.46[/align] [/td][/tr][/table][b]4.2 血浆样品[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模结果4.2.1“吸光度-浓度变化率”方法在血浆蛋白含量建模中的应用[/b]利用“吸光度-浓度变化率”方法对血浆样品进行数据分析,得到每个波数点下的V[sub]mean[/sub]值如图4-3所示,按照其V[sub]mean[/sub]值由大到小排列波数点,依次递增波数点个数进行建模,即得到不同[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型结果。[align=center][img=,653,353]https://ng1.17img.cn/bbsfiles/images/2019/08/201908161624210201_7336_3237657_3.png!w653x353.jpg[/img][/align][align=center]图4-3血浆样品不同波数点的V[sub]mean[/sub]值[/align][url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]血浆蛋白含量建模结果如图4-4所示,最小的RMSEP值为0.495,模型的RPD值为23.535>3,无模型过拟合现象,所涉及变量数为50个,具体波数点如表4-2所示。获得最佳模型的波数点大部分都分布在6200-6400cm[sup]-[/sup][sup]1[/sup],分析此处的特征吸收峰信息,多为N-H的一级倍频信息。[align=center][img=,653,353]https://ng1.17img.cn/bbsfiles/images/2019/08/201908161625411205_2487_3237657_3.png!w653x353.jpg[/img][/align][align=center]图4-4 血浆蛋白样品[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析技术的建模结果[/align][align=center]表4-2血浆蛋白样品进行[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]分析技术的建模变量[/align] [table][tr][td] [align=center]波数(cm[sup]-[/sup][sup]1[/sup])[/align] [/td][td] [align=center]波数(cm[sup]-[/sup][sup]1[/sup])[/align] [/td][td] [align=center]波数(cm[sup]-[/sup][sup]1[/sup])[/align] [/td][td] [align=center]波数(cm[sup]-[/sup][sup]1[/sup])[/align] [/td][td] [align=center]波数(cm[sup]-[/sup][sup]1[/sup])[/align] [/td][/tr][tr][td] [align=center]6363.940[/align] [/td][td] [align=center]6360.083[/align] [/td][td] [align=center]6321.514[/align] [/td][td] [align=center]6294.515[/align] [/td][td] [align=center]6267.517[/align] [/td][/tr][tr][td] [align=center]6367.797[/align] [/td][td] [align=center]6387.082[/align] [/td][td] [align=center]6317.657[/align] [/td][td] [align=center]6414.080[/align] [/td][td] [align=center]6425.651[/align] [/td][/tr][tr][td] [align=center]6371.654[/align] [/td][td] [align=center]6390.938[/align] [/td][td] [align=center]6313.800[/align] [/td][td] [align=center]6417.937[/align] [/td][td] [align=center]6263.660[/align] [/td][/tr][tr][td] [align=center]6356.226[/align] [/td][td] [align=center]6340.798[/align] [/td][td] [align=center]6402.509[/align] [/td][td] [align=center]6290.658[/align] [/td][td] [align=center]6259.803[/align] [/td][/tr][tr][td] [align=center]6375.511[/align] [/td][td] [align=center]6336.941[/align] [/td][td] [align=center]6309.943[/align] [/td][td] [align=center]6286.801[/align] [/td][td] [align=center]7208.608[/align] [/td][/tr][tr][td] [align=center]6352.369[/align] [/td][td] [align=center]6329.228[/align] [/td][td] [align=center]6406.366[/align] [/td][td] [align=center]6282.944[/align] [/td][td] [align=center]6255.946[/align] [/td][/tr][tr][td] [align=center]6348.512[/align] [/td][td] [align=center]6333.084[/align] [/td][td] [align=center]6306.086[/align] [/td][td] [align=center]6421.794[/align] [/td][td] [align=center]6429.508[/align] [/td][/tr][tr][td] [align=center]6379.368[/align] [/td][td] [align=center]6398.652[/align] [/td][td] [align=center]6302.229[/align] [/td][td] [align=center]6279.087[/align] [/td][td] [align=center]6252.089[/align] [/td][/tr][tr][td] [align=center]6383.225[/align] [/td][td] [align=center]6394.795[/align] [/td][td] [align=center]6410.223[/align] [/td][td] [align=center]6275.230[/align] [/td][td] [align=center]7204.751[/align] [/td][/tr][tr][td] [align=center]6344.655[/align] [/td][td] [align=center]6325.371[/align] [/td][td] [align=center]6298.372[/align] [/td][td] [align=center]6271.374[/align] [/td][td] [align=center]6433.365[/align] [/td][/tr][/table][b]4.2.2 同常规波段选择方法的[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模比较[/b]为考察“吸光度-浓度变化率”方法的预测能力高低,将其同其他常规变量选择方法 (FiPLS, BiPLS, CC, UVE) 对相同光谱数据进行处理,建立的近红外模型结果对比如图4-5所示。从图4-5中可明显看出,同其他变量选择方法相比,RATC得到了最小的RMSEP值(RMSEP=0.495g/L)。综上所述,对于原料人血浆样品的总蛋白定量来说,RATC方法减少了参与[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模的变量数,提高了血浆蛋白含量建模的预测能力,是一种有效的变量选择方法。[align=center][img=,622,370]https://ng1.17img.cn/bbsfiles/images/2019/08/201908161626000014_401_3237657_3.png!w622x370.jpg[/img][/align][align=center]图4-5 不同血浆蛋白含量的[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模结果比较[/align][align=center][b] [/b][/align][b]5小结[/b]本文基于吸光度浓度变化率来对校正样品集中所有样品进行波段选择;其过程为:预先设定校正样品集中共有n个样品,每个样品光谱中共有N个变量,对于校正样品集所有样品来说,每个变量则有n个吸光值和n个浓度值;其中,N和n均为大于1的正整数;依次计算每个变量下相邻样品的吸光值差值和浓度差值的比值V,最终在每个变量下得到(n-1)个比值V,再计算所有比值V的平均值V[sub]mean[/sub];对于校正样品集中样品光谱的N个变量,得到N个V[sub]mean[/sub]值,将N个变量按照其V[sub]mean[/sub]值进行排序;按照V[sub]mean[/sub]值由大变小的顺序依次选择出相应变量,直至所有变量全部选完,停止建模,记录所有情况的建模结果。同常规波段选择方法比较,该方法从三个方面进行了改进,不仅减少了参与[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]建模变量的数目,提高了[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型的预测能力。丰富了[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型的波段选择方法,给[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]模型使用者提供“吸光度-浓度变化”波段选择方法。同时由于是根据物质的[url=https://insevent.instrument.com.cn/t/1p][color=#3333ff]近红外光谱[/color][/url]吸光度和浓度的关系建立的波段选择方法,某种程度上,该方法更能够反应物质的化学信息,即吸光度随着浓度变化率,使得该波段选择方法具有广泛的可行性和通用性。





