

表 1 8大类脂质分子
类别 | 缩写 | 数据库中的结构数量 |
脂肪酰类(Fatty acyls) | FA | 2678 |
甘油脂类(glycerolipids ) | GL | 3009 |
甘油磷酸脂类(glycerophospholipids) | GP | 1970 |
鞘脂类(sphingolipids ) | SP | 620 |
固醇脂类(sterol lipids ) | ST | 1744 |
异戊烯醇脂类(prenol lipids () | PR | 610 |
糖脂类(saccharolipids ) | SL | 11 |
多聚乙烯类(polyketides ) | PK | 132 |
表1 脂质组学研究的工作流程
从患者得到脂质组学研究的样品 | |
液体 | 固体 |
体液,泪水,血清,血浆,尿液 (低温保存样品) | 细胞,组织,器官 |
对上述样品进行萃取方法 | |
| 对极性化合物,单独的有机化合物进行: 液-液萃取,固相萃取 | 对能源性物质进行:加压液相萃取,微波辅助萃取,超声辅助萃取 |
萃取得到的脂质化合物 | |
| 使用色谱方法分离:气相色谱,液相色谱,电泳 | 不使用色谱方法分离:直接进样,成像 |
上述分离或未分离样品进行质谱分析 | |
质谱分析的接口 | 质量分析器 |
| 电子轰击电离(EI),电喷雾电离(ESI),化学电离(CI),大气压(APCI)化学与电离,基质辅助激光解析电离(MALDI) | 四级杆飞行时间质谱(qTOF),三重四级杆质谱( qqq),轨道阱质谱(Orbitrap) |
质谱原始数据语预处理 (利用商品或自制软件) | |
分类和脂质鉴定(使用各种资源如LIPID maps,Lipid Bank,Lipid Blast) | |
判定在疾病中的机制/在疾病演化中的作用 | |
为进一步诊断找出生物标记物(预防),提供药物治疗的指导 | |
表2 脂质组学研究中的样品处理方法比较(Chin Chye Teo et al,TrAC,2015,65:1-18)
| 萃取方法 | 临床样品类型 (生物液体或固体) | 优点 | 缺点 | 原文文献编号 |
| 单一有机溶剂萃取(SOSE) | 血清(生物液体) 皮肤(固体) | 容易完成 萃取时间短 成本低 低温适于热敏感化合物 无需外部能量 | 使用有毒有机溶剂 分析时难以摆脱使用有机溶剂 | 1.2 3 |
| 液-液萃取(LLE) | 眼泪(生物液体) 血清(生物液体) 血浆(生物液体) 尿液(生物液体) 滑液(生物液体) 动脉粥样硬化血小板(生物液体) 皮肤(固体) 组织(固体) | 易于建立的方法 容易完成 设备便宜 萃取时间短 使用廉价溶剂(如甲醇,水) 低温适于热敏感化合物 无需外部能量 萃取时间短 | 使用大量有毒有机溶剂 常使用超过一种类型的溶剂 需要排除溶剂以免影响分析 | 2 4,9-13 5,14-22 8,23 7 24 25-27 28,29 |
| 固相萃取(SPE) | 血清(生物液体) 血清(生物液体) 血浆(生物液体) 眼(固体) 皮肤(固体) | 容易完成 清除干扰基体 EPE的选择 低温适于热敏感化合物 萃取时间短 | SPE萃取小柱比较贵 需要洗掉有机溶剂以免影响分析 使用有毒有机溶剂 分析时难以摆脱使用有机溶剂 | 1,12 2 30 26 3,27 |
| 固相微萃取(SPME) | 肺(固体) 头发(固体) | 容易完成 可与gc和gc xgc 联用 对挥发性化合物可以进行顶空气相色谱 有毒溶剂消耗量少 低温适于热敏感化合物 无需外部能量 萃取时间短 | 萃取头比较贵 需要洗掉有机溶剂以免影响分析 分析时难以摆脱使用有机溶剂 | 31 32 |
| 超临界流体萃取(SFE) | 血浆(生物液体) | 容易完成 萃取时间短 对非极性化合物萃取效率高 CO2可循环使用 温度压力可控 可加改性剂提高萃取液极性和效率 | 要精心操作 设备昂贵 | 33 |
| 微波辅助萃取(MAE) | 血浆(生物液体) 皮肤(固体) | 容易完成 萃取时间短 萃取效率高 萃取溶剂消耗量少 温度压力可控 | 需要冷却防止溶剂逃逸 购买设备费用高 | 34 35 |
| 超声辅助萃取(UAE) | 血(生物液体) | 容易完成 萃取时间短 萃取溶剂消耗量少 温度压力可控 | 听力会受损 要使用有毒有机溶剂 会吸入有害溶剂 需要外部能源 购买设备费用高 提高温度会使化合物降解 | 36,37 |
下表列出不同样品容积需要加入的试剂量
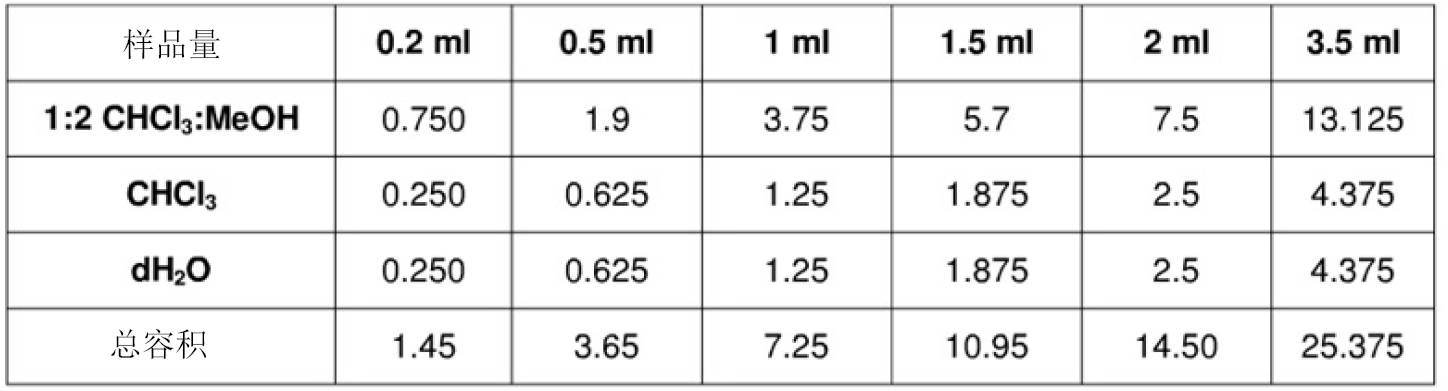
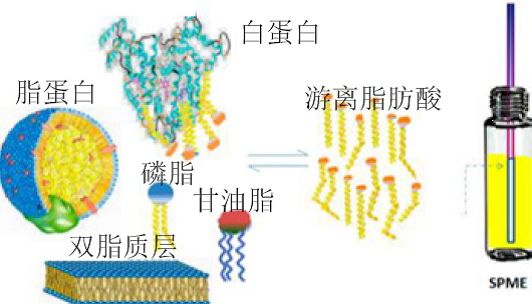
(Anal Chem, 2014, 86:12022-12029)
表2中的文献
1 | Stubiger G, et al, Atherosclerosis, 2012,224:177-186. |
2 | Zhao Z, et al, J Lipid Res, 2010, 51:652-659 |
3 | t’Kindt R, et al, Anal Chem, 2012,84:403-411 |
4 | Cui L, et al, PLoS Negl Trop Dis,2013,7:e2373 |
5 | Sandra K,et al, J Chromatogr A,2010,1217:4087-4099. |
6 | Lam S M, et al, J Lipid Res, 2014,55: 289-298 |
7 | Giera M, et al, Biochim Biophys Acta, 2012, 1821:415-424 |
8 | Min H K, Anal Bioanal Chem, 2011, 399:823-830. |
9 | Heilbronn L K, et al, Obesity,2013, 21:E649-E659 |
10 | Hilvo M, et al, Int J Cancer 134 (2014) 1725-1733 |
11 | Montoliu I, et al, Aging (Albany NY),2014,6:9-25 |
12 | Chen Y , et al, Clin. Chim. Acta, 2013,428: 20-25. |
13 | Zivkovic A M, et al, Metabolomics,2009,5:507-516 |
14 | Chen F,et al, Biomarkers, 2011, 16:321-333 |
15 | M. Ollero, et al, J. Lipid Res, 2011, 52:1011-1022 |
16 | Shah V, Rapid Commun. Mass Spectrom, 2013, 27:2195-2200 |
17 | Lankinen M, et al, PLoS ONE, 2009,4:e5258. |
18 | J. Graessler, et al, PLoS ONE,2009, 4:e6261 |
19 | Lofgren L et al,, J Lipid Res, 2012,53:1690-1700 |
20 | Gurdeniz G, et al, PLoS ONE, 2013,8:e69589. |
21 | Zhou X, et al, PLoS ONE, 2012, 7:e48889. |
22 | Bui H H, et al, Anal Biochem, 2012,423:187-194. |
23 | Kim H, et al, Analyst, 2008, 133:1656-1663. |
24 | Stegemann C, et al, Circ Cardiovasc Genet, 2011,4:232-242. |
25 | van Smeden J, et al, J Lipid Res, 2011,52:1211-1221. |
26 | Acar N, et al, PLoS ONE,2012, 7:e35102. |
27 | Shin J H, et al, Anal Bioanal Chem,2014,406:1917-1932 |
28 | Cheng H, et al, J Neurochem, 2013,127:733-738. |
29 | Pietilainen K H,et al, PLoS Biol,2011, 9:e1000623. |
30 | Cha D, et al, J Chromatogr A,2009,1216:1450-1457. |
31 | Cha D, et al, Anal Chim Acta,2006, 572: 47-54. |
32 | Pragst F, et al, Forensic Sci Int,2010, 196: 101-110 |
33 | Uchik T,et al, J. Chromatogr A, 2012,1250:69-75. |
34 | de Morais D R, et al, Rev Bras Hematol Hemoter,2010,32:439-443. |
35 | Gonzalez-Illan F,et al,J Anal Toxicol,2011,35:232-237. |
36 | Pizarro C, et al, Anal Chem,2013,8:12085-12092. |
37 | Pang L Q, et al, J Chromatogr B,2008,869: 118-125 |